Ein Bild vom Kampf zwischen Virus und Wirtszelle
07/10/2019Würzburger Wissenschaftler haben die Aktivität tausender Gene in einzelnen Zellen über Stunden präzise verfolgt. Erstmals konnten sie zeigen, warum manche Zellen von Viren erfolgreich infiziert werden, andere hingegen nicht.
Dringen Viren in unseren Körper ein – etwa bei einer Grippe oder einem Magen-Darm-Infekt – verändern sich die Abläufe in den betroffenen Zellen: Im ungünstigsten Fall übernimmt das Virus das Ruder, und die Zelle wird umprogrammiert. Sie produziert dann Virus-Bestandteile, und der Eindringling vermehrt sich explosionsartig. In einer anderen Zelle zieht aber womöglich das Virus den Kürzeren und wird durch die aktivierten Schutzmechanismen erfolgreich eliminiert.
Doch wie kommt es, dass die eine Zelle überrannt wird und die andere das Virus unter Kontrolle bringt? Wie schnell reagieren einzelne Zellen auf einen Virusangriff und welche schützenden Gene werden aktiviert? Diese Fragen haben Wissenschaftler der Julius-Maximilians-Universität Würzburg und des Helmholtz-Instituts für RNA-basierte Infektionsforschung (HIRI) in Würzburg untersucht. Mit Hilfe einer neuen, von ihnen entwickelten Methode konnten sie die Aktivität tausender Gene in einzelnen Zellen untersuchen und über einige Stunden präzise verfolgen. Damit konnten sie erstmals zeigen, warum manche Zellen erfolgreich von einem Virus infiziert werden, andere hingegen nicht. Darüber hinaus gewannen sie grundlegend neue Erkenntnisse über die Regulation von Genen. Ihre Ergebnisse sind in der aktuellen Ausgabe des Fachmagazins Nature veröffentlicht.
Forschung am Zytomegalievirus
In enger Zusammenarbeit mit Professor Florian Erhard vom Institut für Virologie und Immunbiologie der Julius-Maximilians-Universität Würzburg (JMU) und Dr. Antoine-Emmanuel Saliba vom Helmholtz-Institut für RNA-basierte Infektionsforschung (HIRI) untersuchte das Forscherteam um Professor Lars Dölken, dem Inhaber des Lehrstuhls für Virologie an der JMU, wie sich die Genaktivität – die die Identität und den physiologischen Zustand einer Zelle widerspiegelt – nach einer Infektion mit dem Zytomegalievirus innerhalb einzelner infizierter Mauszellen verändert. Zytomegalieviren sind weit verbreitet, über 80 Prozent der Menschen sind infiziert. Gesunden können sie in der Regel nichts anhaben, für Neugeborene oder Transplantationspatienten kann eine Infektion aber gefährlich werden und schwerwiegende neurologische Folgen nach sich ziehen.
Mit einem häufig eingesetzten experimentellen Verfahren, der sogenannten Einzelzell-RNA-Sequenzierung (scRNAseq), ist es möglich zu bestimmen, welche Gene einer Zelle gerade aktiv sind. Kurzfristige Änderungen von Genaktivitäten, wie sie etwa bei einer Virusinfektion auftreten, können damit aber nur sehr begrenzt aufgespürt werden. Zudem kann jede einzelne Zelle nur einmal untersucht werden. Somit blieb bisher unklar, wie einzelne Zellen auf äußere Einflüsse, zum Beispiel eine Virusinfektion, reagieren.
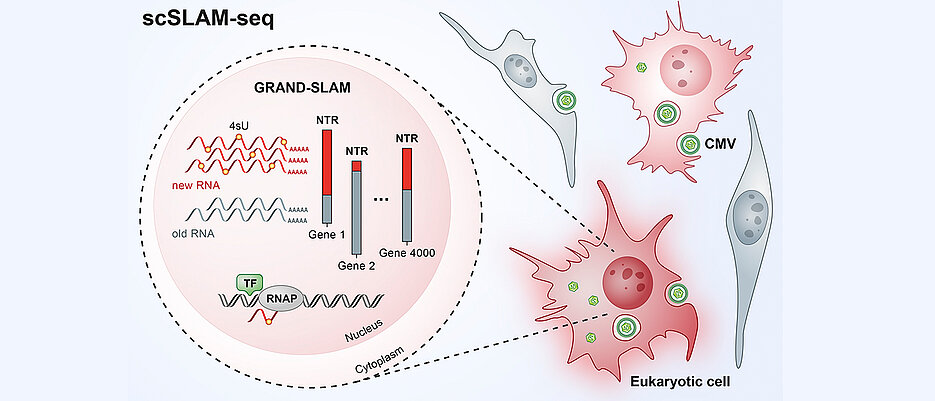
Um die molekularen Vorgänge innerhalb einzelner infizierter Zellen zu untersuchen, entwickelten die Forscher nun eine neue Methode namens scSLAM-seq, mit der sie erstmals sichtbar machen können, welche Gene wie stark in einzelnen Zellen innerhalb weniger Stunden aktiviert werden. Wird ein Gen aktiviert, wird sein Code in RNA (englisch: ribonucleic acid) übersetzt. Die RNA besteht aus vier unterschiedlichen Bausteinen, den organischen Basen Adenin, Cytosin, Guanin und Uracil. Diese sind wie auf einer Kette aufgereiht, und zwar in einer für das Ursprungsgen charakteristischen Kombination. Die RNA-Kette dient dann als Vorlage für die Herstellung eines Proteins, das eine bestimmte Funktion innerhalb der Zelle erfüllt.
scSLAM-seq sortiert RNA in alt und neu
Um unterscheiden zu können, welche RNA vor der Virusinfektion bereits vorhanden war und welche neu hinzugekommen ist, bedienten sich die Forscher eines Markierungstricks: Sie fügten zeitgleich mit dem infizierenden Virus eine im Vergleich zur natürlichen Variante chemisch leicht veränderte Form des RNA-Bausteins Uracil zum Nährmedium der Zellen hinzu. Die Zellen bauten daraufhin das markierte Uracil in ihre neu hergestellte RNA ein. Nach zwei Stunden wurde das Experiment beendet. Über eine chemische Reaktion wurde das markierte Uracil in einen anderen RNA-Baustein, nämlich Cytosin, umgewandelt. „In der RNA-Sequenz befindet sich dort, wo eigentlich Uracil eingebaut sein sollte, dann stattdessen Cytosin“, erklärt Dölken. „Die Idee, die dahintersteckt: Die RNA, die nach der Virusinfektion hergestellt wurde, besitzt nun eine Markierung, mit der wir sie bei der anschließenden RNA-Sequenzierung als neu identifizieren können.“
Mithilfe eines komplexen bioinformatischen Verfahrens untersuchten die Forscher die RNA jeder einzelnen Zelle, ordneten sie über 4000 bekannten Genen pro Zelle zu und trennten sie in neue und alte RNA auf. „Die Daten, die wir mit dem scSLAM-seq-Verfahren erheben können, sind spektakulär“, sagt Erhard. „Wir können tatsächlich für jede einzelne Zelle feststellen, wie viel Prozent ihrer RNA innerhalb von zwei Stunden nach einer Störung – in diesem Fall einer Virusinfektion – neu hergestellt werden. Damit sind erstmals Dosis-Wirkungs-Analysen auf Einzelzellebene möglich.“
Insgesamt untersuchte das Forscherteam die RNA von 100 Einzelzellen. „Das war bereits ausreichend, um einen gänzlich neuen Einblick in die zelluläre Genaktivierung zu bekommen“, sagt Saliba. „Mittels scSLAM-seq können wir nun erstmals präzise analysieren, wie eine einzelne Zelle innerhalb eines kurzen Zeitfensters auf eine Störung wie etwa eine Virus- oder Bakterieninfektion reagiert, welche Gene in der Folge vermehrt oder vermindert abgelesen werden, und so nachvollziehen, welchen Schlachtplan sie im Kampf gegen den Eindringling vorbereitet hat.“
Jede Zelle tickt anders
Weiterhin konnten die Wissenschaftler zeigen, dass das Ablesen von Genen nicht kontinuierlich abläuft, sondern in Schüben (englisch: bursts): So weckt die Virusinfektion hunderte Gene aus ihrem Dornröschenschlaf und bewirkt ihre Ablesung binnen Stunden nach Eindringen des Virus in die Zelle. Dabei werden vor allem solche Gene aktiviert, die unseren Zellen helfen, die Infektion zu bekämpfen. „In unseren Analysen zeigten viele zelluläre Gene ein ausgeprägtes Burst-Verhalten. Entweder war in einer Zelle fast die gesamte RNA eines Gens neu oder alt“, sagt Erhard. „Und wir konnten zeigen, dass das Burst-Verhalten von der Struktur bestimmter Regionen der Gensequenz – sogenannten Promotoren – abhängt, die das Ablesen der Gene steuern.“
Diese wird also nicht rauf- oder runterreguliert, sondern erfolgt in jeder Zelle nach einem On/Off-Prinzip. Saliba: „Das erklärt auch, warum sich Zellen in ihren RNA-Profilen häufig so deutlich unterscheiden und manche Zellen etwa sofort gegen Viren angehen können und andere zu dem Zeitpunkt noch nicht.“ Jede Zelle tickt also nach ihrem eigenen Takt: So weisen Zellen mit zunächst identischen RNA-Profilen bereits nach wenigen Tagen komplett unterschiedliche RNAs in ihrem Zellinnern auf. Dölken: „Mit unseren Untersuchungen konnten wir grundlegend neue Erkenntnisse zur Taktung der zellulären Genaktivierung gewinnen, die mein Verständnis darüber tatsächlich komplett verändert haben.“
Schutz vor Autoimmunerkrankungen
Das On/Off-Prinzip der zellulären Genaktvierung hat für unseren Körper wahrscheinlich eine ganz wichtige Funktion. Denn würden alle Gene, die dem Kampf gegen Viren dienen, dauerhaft von jeder Körperzelle produziert, könnte es zu Fehlreaktionen und Autoimmunerkrankungen kommen. „Durch dieses Anschalten im richtigen Moment, nach dem Motto ‚Wasser Marsch!‘ – aber eben nur wenn es brennt – kann unser Immunsystem eine schützende Umgebung aufbauen, ohne Risiko schädlicher Fehlreaktionen“, sagt Dölken. So stehen nur in einem kleinen Teil der Körperzellen bestimmte Mechanismen voll funktionsfähig bereit. Diese „Sentinel“-Zellen sind dann in der Lage, zum Beispiel ein eindringendes Virus zu erkennen und effizient zu bekämpfen. Und sie informieren die anderen Zellen, die dann ebenfalls das komplette Abwehrarsenal hochfahren und entsprechende Gene aktivieren, um die Infektion zu kontrollieren und die Gefahr zu bannen.
Mit dem zum Patent angemeldeten bioinformatischen Analyse-Verfahren, das zur Auswertung der hochkomplexen experimentellen Daten nötig ist, konnten die Würzburger Forscher grundlegend neue Einblicke in zelluläre Abläufe gewinnen. „Erstmals können wir wirklich sehen, wie eine einzelne Zelle reagiert“, sagt Dölken. In zukünftigen Untersuchungen kann es zur Beantwortung unterschiedlichster Fragestellungen auf Einzelzellebene genutzt werden. „scSLAM-seq eignet sich hervorragend für Knock-Out-Untersuchungen, um herauszufinden, welche Gene für die Bekämpfung von Krankheitserregern oder bei der Entstehung von Erkrankungen eine Schlüsselrolle spielen“, sagt Saliba. „Es ist methodisch einfach, die Datenqualität ist hoch und ideal für Dosis-Wirkungs-Untersuchungen, auch über die Zeit.“ Das Forschertrio ist sich daher sicher: Es wird spannend!
Kontakt
Prof. Dr. Lars Dölken, Lehrstuhl für Virologie, Universität Würzburg, T (0931) 31-89781, lars.doelken@uni-wuerzburg.de